Détails des projets
Informations du projet
- Catégories : scRNA-seq, QC, Clustering
- Laboratoire : Tutorat académique
- Date :
- URL projet : doc_pp
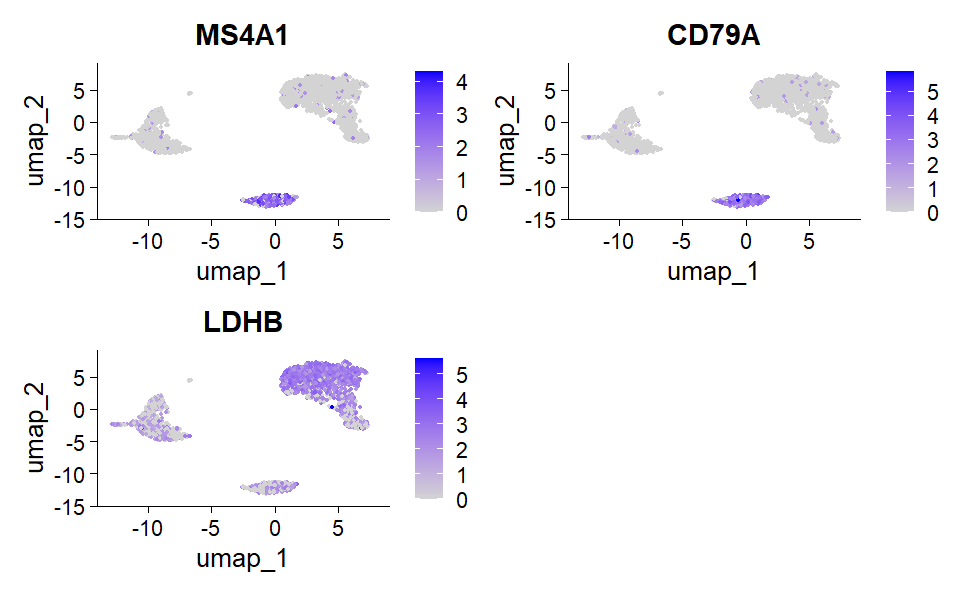
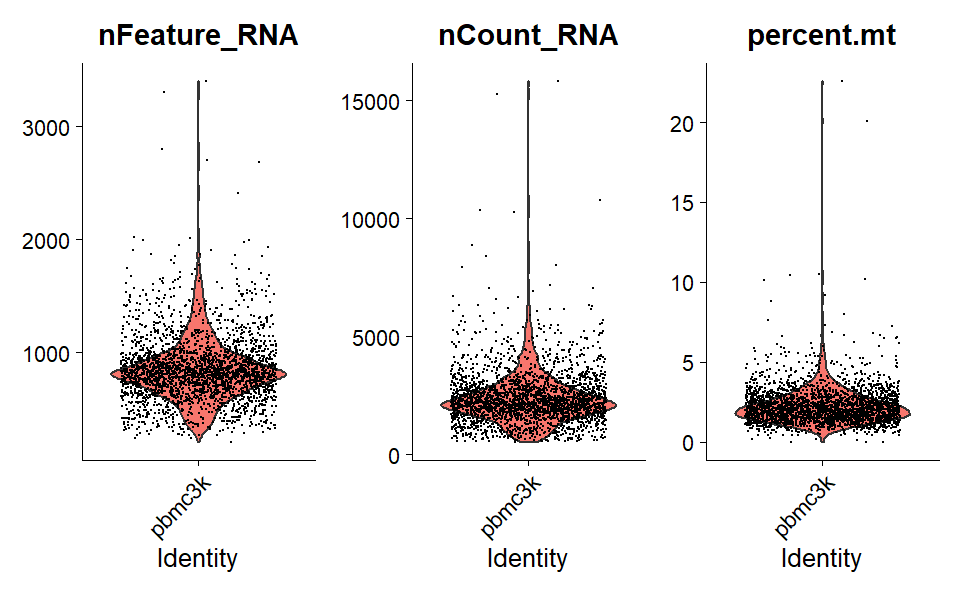
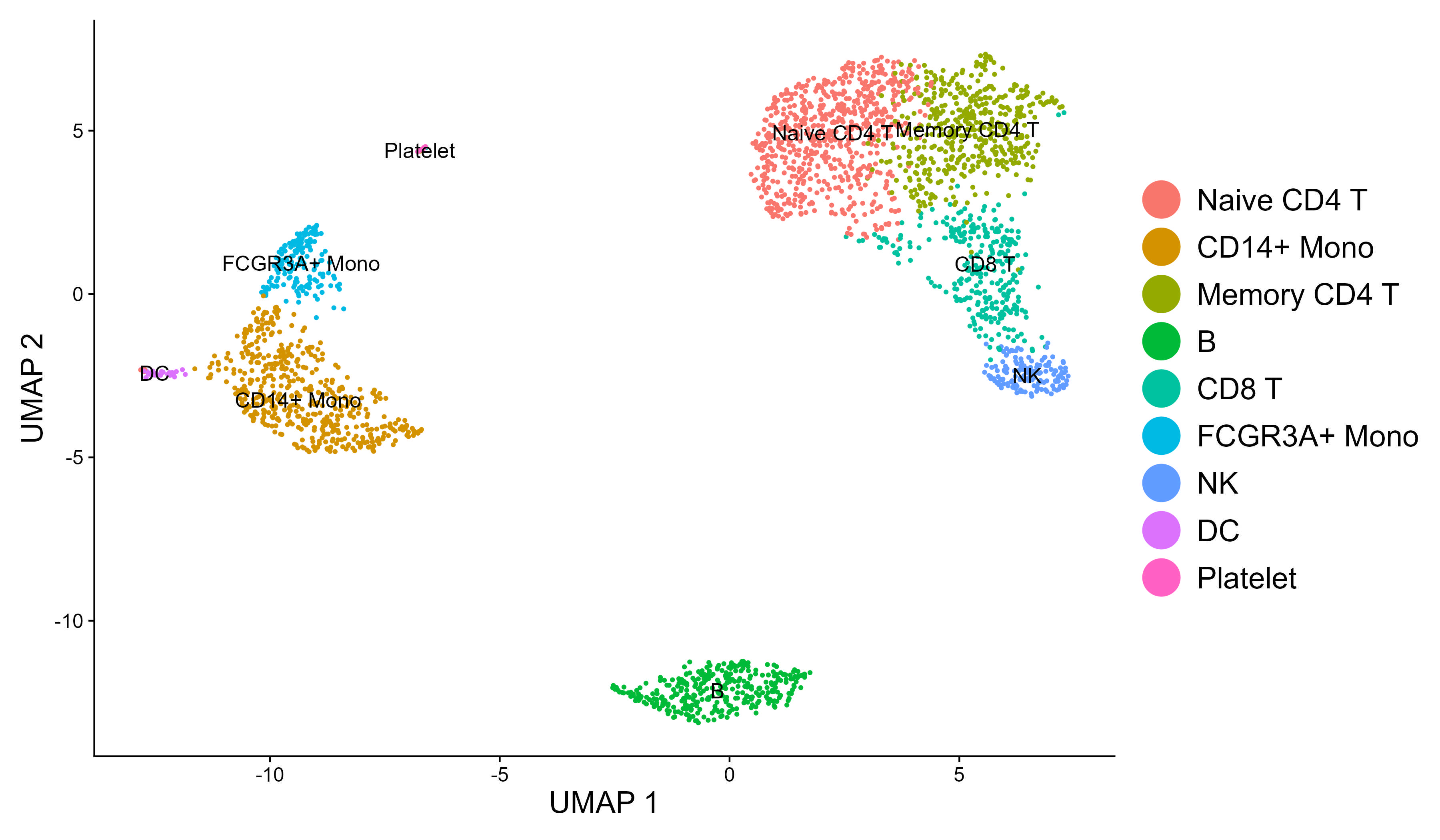
Pipeline scRNA-seq — PBMC
Prétraitement (filtrage UMI/gènes/MT%), normalisation, réduction dimensionnelle, clustering et annotation des types cellulaires. Identification des gènes marqueurs par cluster et visualisations (UMAP, heatmaps).
Informations du projet
- Catégories : bulk RNA-seq, Transposable Elements
- Laboratoire : LBBE
- Date :
- URL projet : doc_soutenance
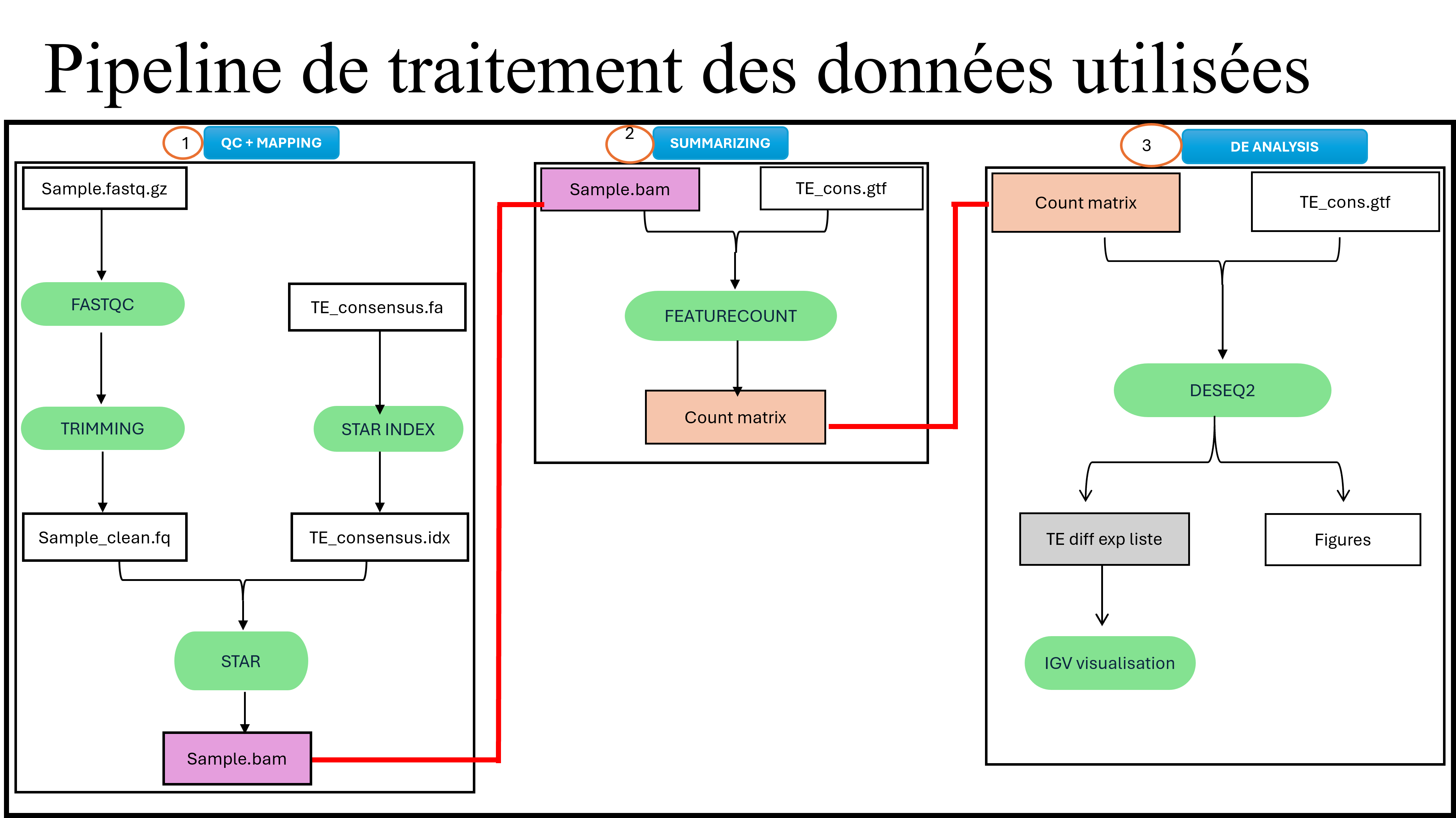
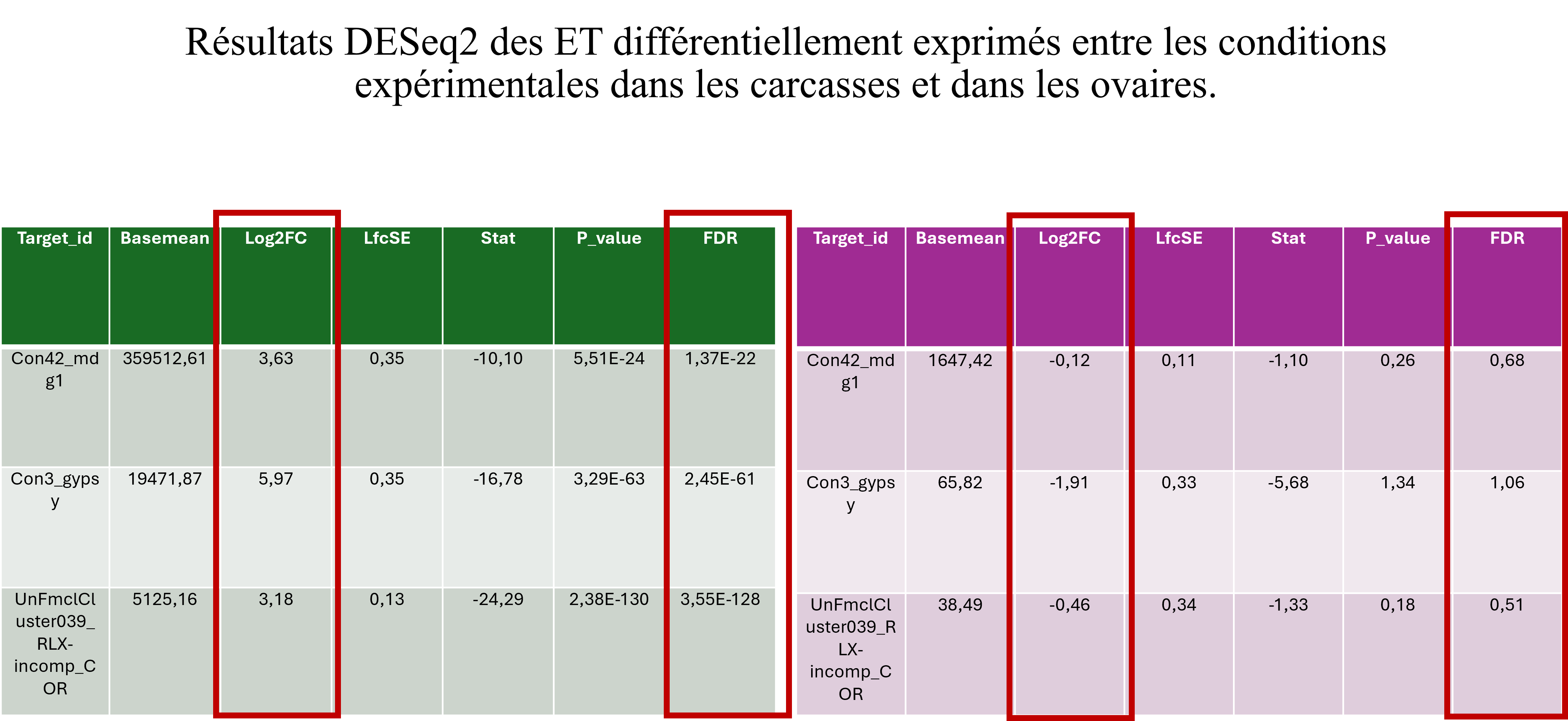
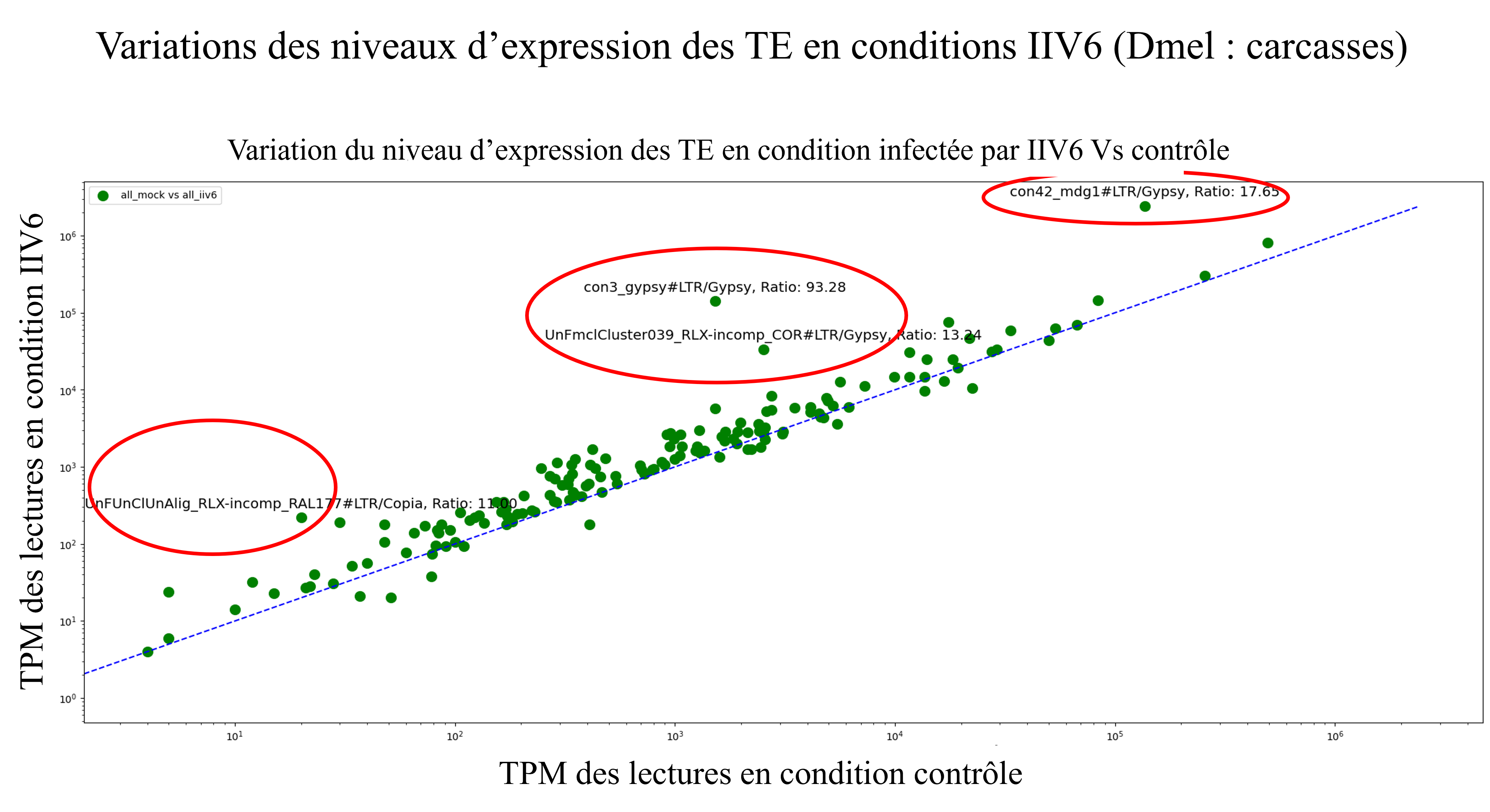
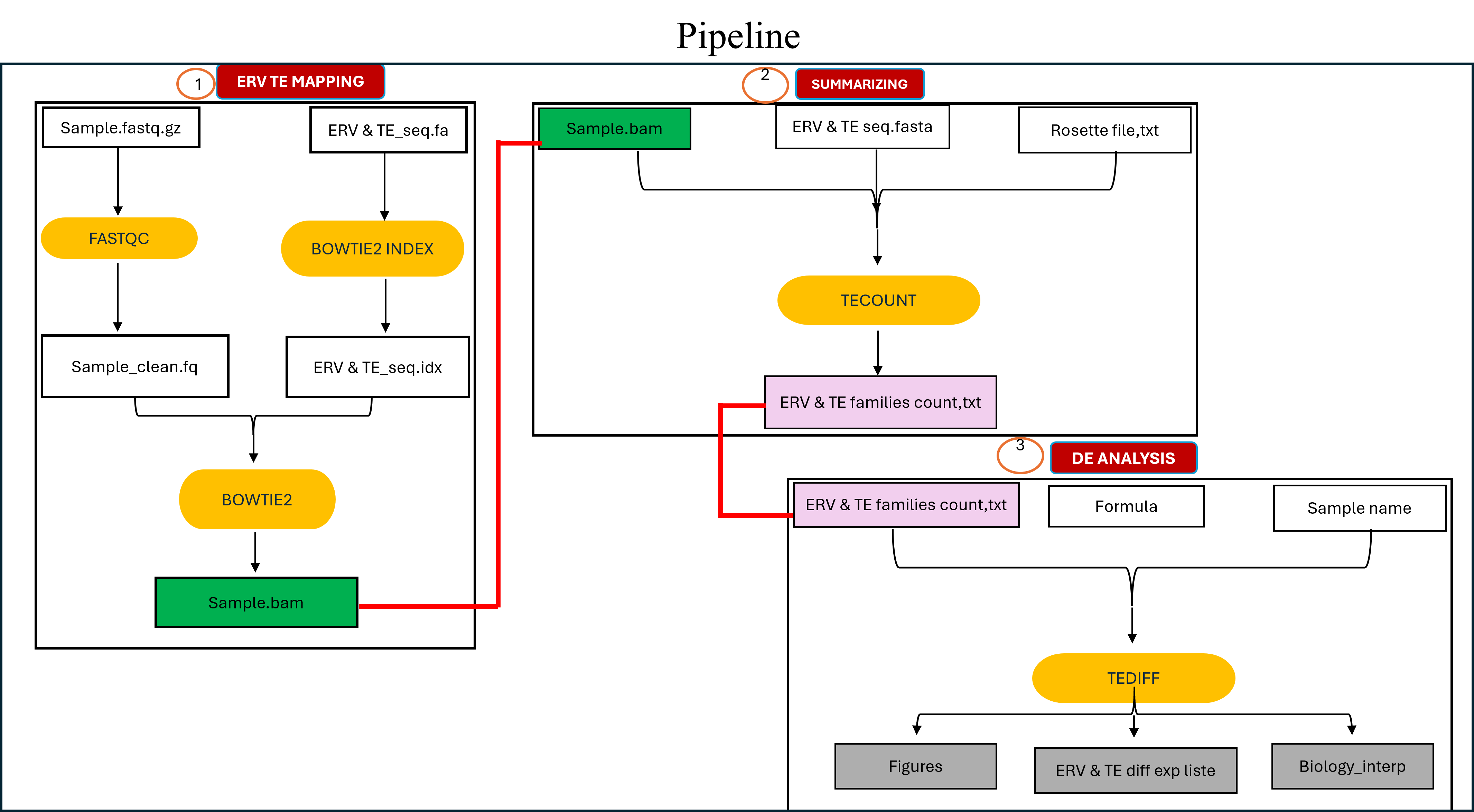
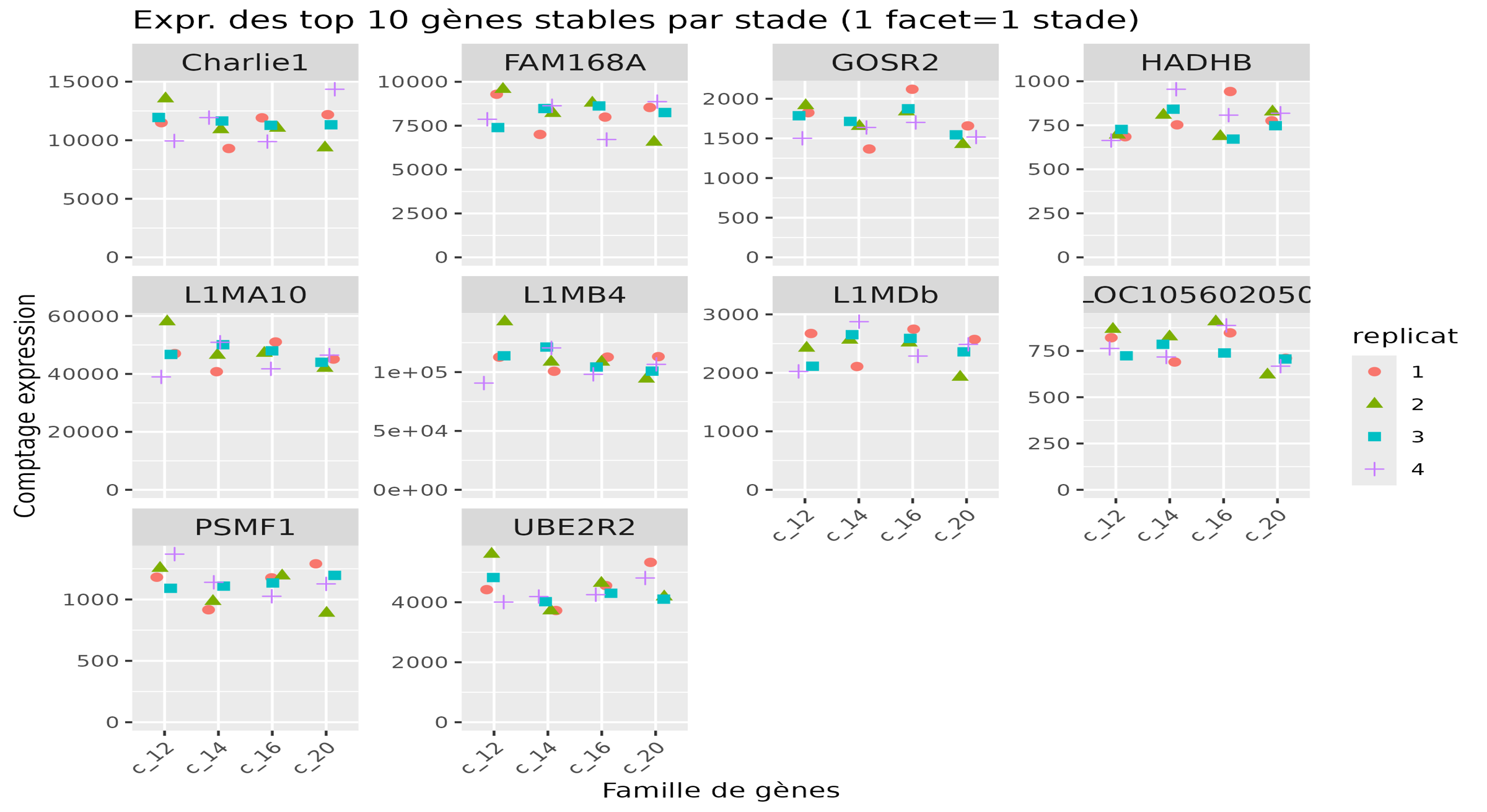
ET & virus IIV6 — Drosophila
Analyse de l’expression des éléments transposables (ET) et étude des insertions potentielles dans le génome viral (IIV6) via données bulk RNA-seq et annotation sous IGV. Mise en évidence d’une surexpression des ET induite par l’infection virale.
Informations du projet
- Catégories : bulk RNA-seq, Pipelines
- Laboratoire : INRAE (IVPC) & LBBE
- Date :
- URL projet : doc_soutenance
ERVII-5 & ERVII-3 — petits ruminants
Étude de l’expression de deux familles de rétrovirus endogènes (ERVII-5 et ERVII-3) chez les petits ruminants afin d’évaluer leur activité transcriptionnelle et leur impact évolutif sur l’expression génique. Analyses réalisées à partir de données RNA-seq, incluant le traitement, la cartographie et la quantification des transcrits. Le projet s’inscrit dans les recherches sur la co-évolution entre les rétrovirus et leurs hôtes.
Informations du projet
- Catégories : Proteomics, Peptide Identification, Phylogeny
- Laboratoire : INRAE
- Date :
- URL projet : GitLab – proteomic-and-defensome-project
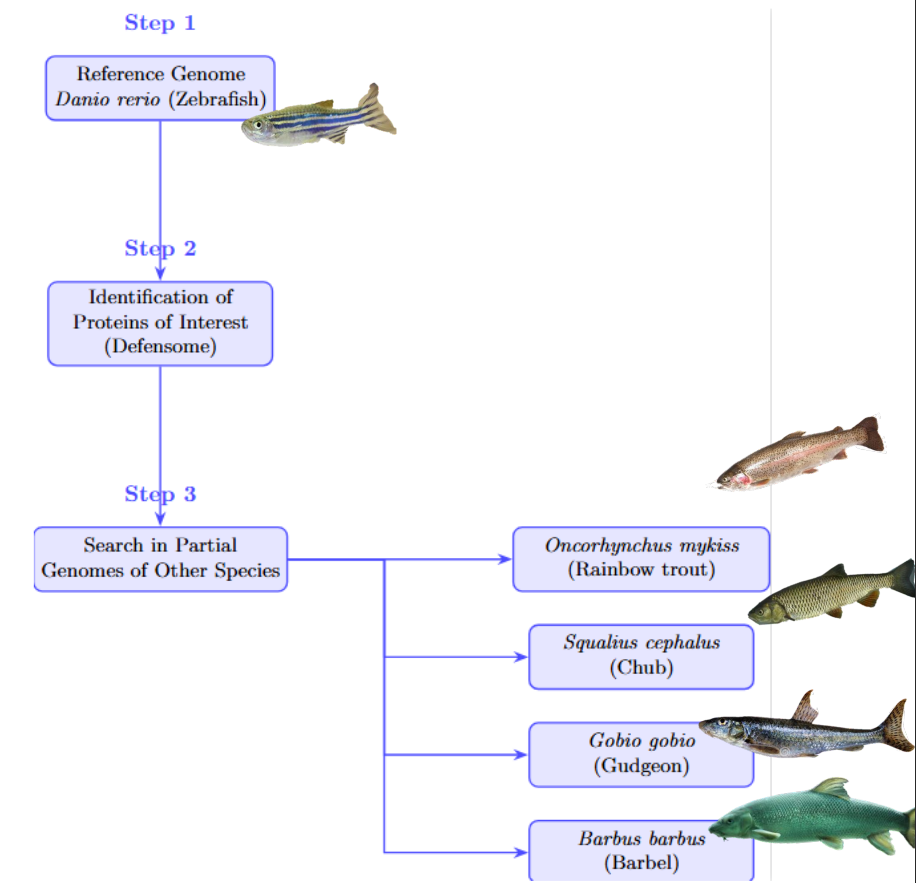
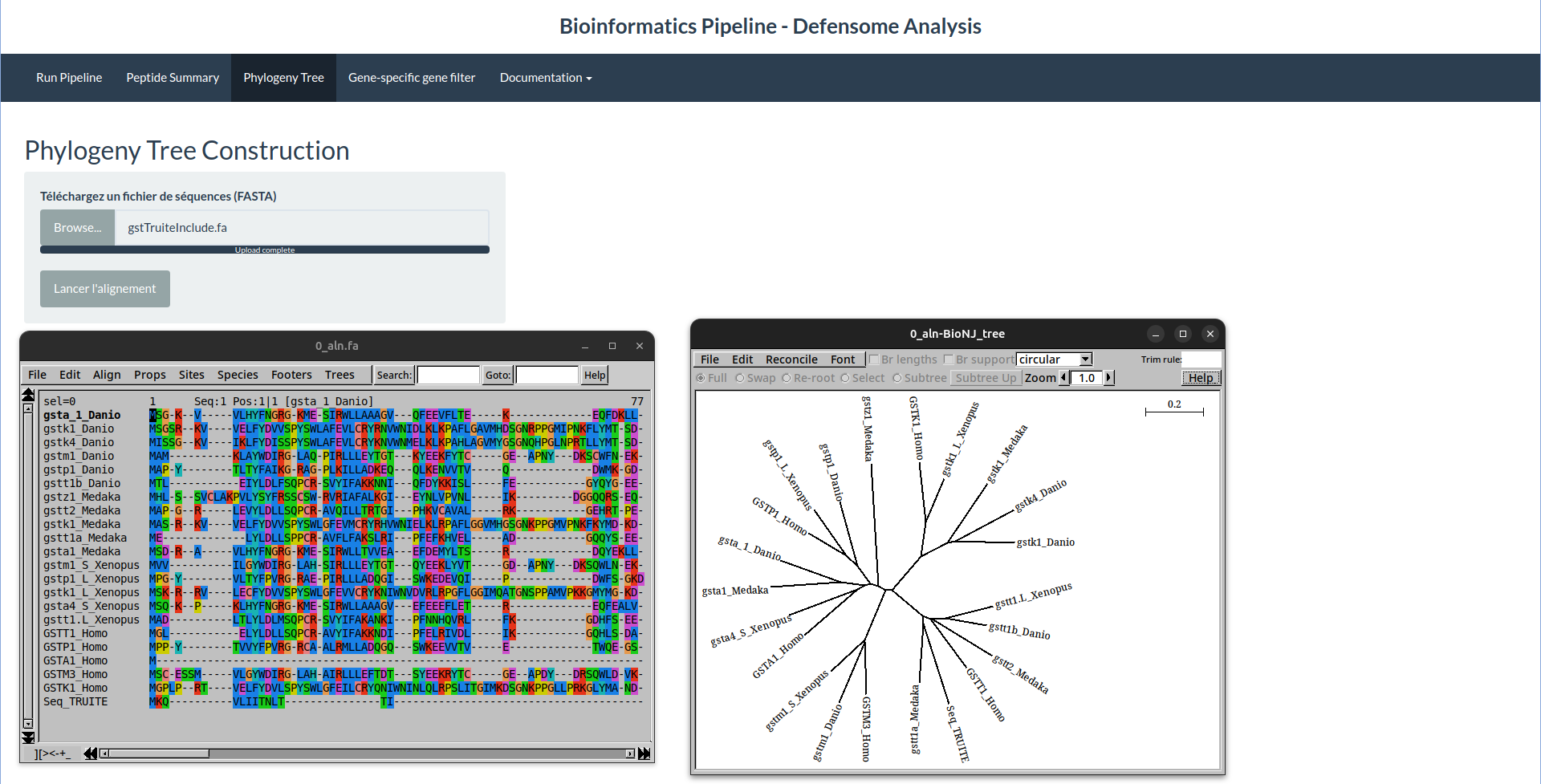
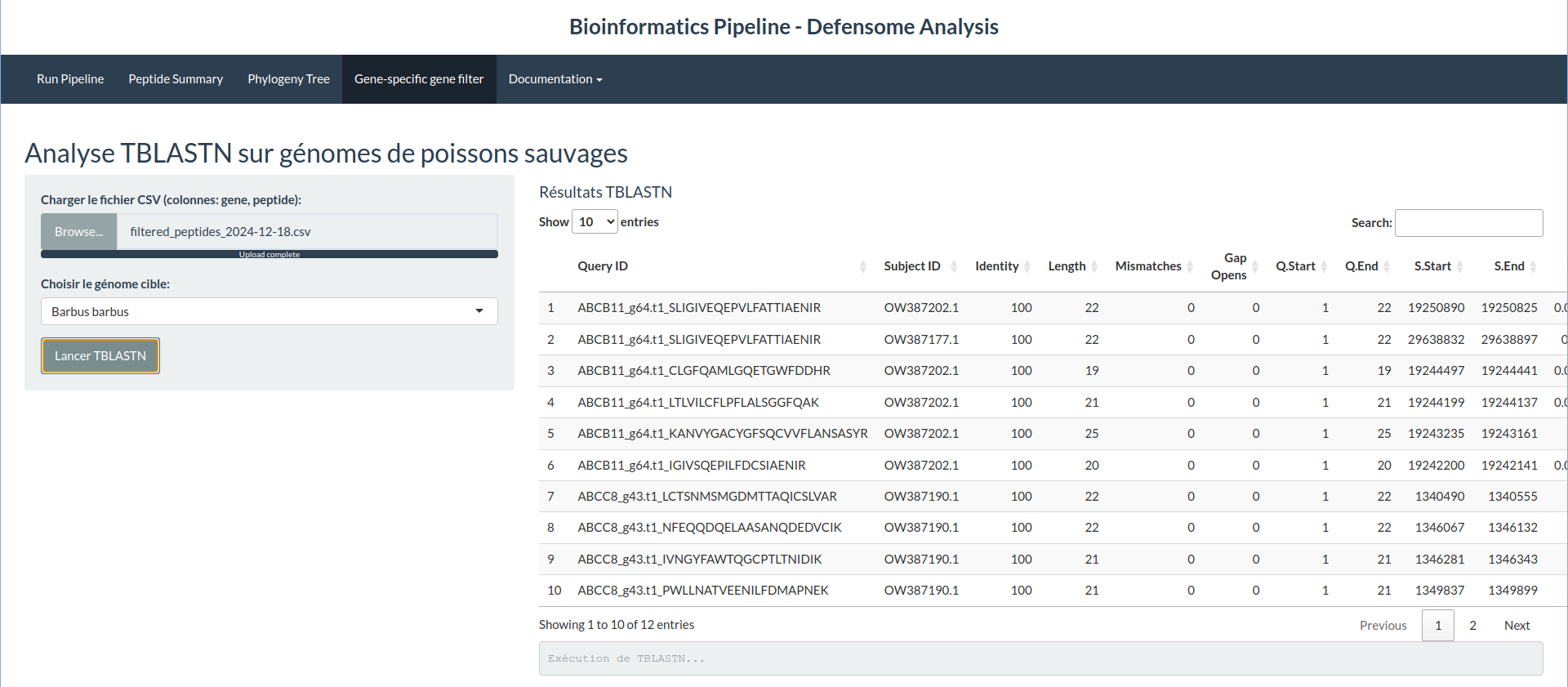
PeptideFinder & Viz interactives
Ce projet se concentre sur l'identification de biomarqueurs protéomiques issus du défensome chimique des espèces de poissons sauvages. En intégrant des outils bioinformatiques et des flux de travail computationnels, nous visons à analyser les données génomiques et protéomiques pour comprendre les réponses de ces espèces aux facteurs de stress environnementaux. Le projet explore également des biomarqueurs potentiels pour la surveillance écologique et l'évaluation des risques.